ФПТМ
дѕУДзіВтЪд
аЗНВюЗжЮі
ФтКЯЯпЕФМђЕЅЭМНт
ФЃаЭЕФpжЕКЭRЦНЗН
МьВщФЃаЭЕФМйЩш
ОпгаШ§РрКЭIIаЭЦНЗНКЭЕФаЗНВюЪОР§ЗжЮі
аЗНВюЗжЮі
ФтКЯЯпЕФМђЕЅЭМНт
зщКЯФЃаЭЕФpжЕКЭRЦНЗН
МьВщФЃаЭЕФМйЩш
дѕУДзіВтЪд
ОпгаСНИіРрБ№КЭIIаЭЦНЗНКЭЕФаЗНВюЪОР§ЕФЗжЮі
БОЪОР§ЪЙгУIIаЭЦНЗНКЭ ЁЃВЮЪ§ЙРМЦжЕдкRжаЕФМЦЫуЗНЪНВЛЭЌЃЌ
Data = read.table(textConnection(Input),header=TRUE) plot(x = Data$Temp, y = Data$Pulse, col = Data$Species, pch = 16, xlab = "Temperature", ylab = "Pulse") legend('bottomright', legend = levels(Data$Species), col = 1:2, cex = 1, pch = 16)
аЗНВюЗжЮі
Anova Table (Type II tests) Sum Sq Df F value Pr(>F) Temp 4376.1 1 1388.839 < 2.2e-16 *** Species 598.0 1 189.789 9.907e-14 *** Temp:Species 4.3 1 1.357 0.2542 ### Interaction is not significant, so the slope across groups ### is not different. model.2 = lm (Pulse ~ Temp + Species, data = Data) library(car) Anova(model.2, type="II") Anova Table (Type II tests) Sum Sq Df F value Pr(>F) Temp 4376.1 1 1371.4 < 2.2e-16 *** Species 598.0 1 187.4 6.272e-14 *** ### The category variable (Species) is significant, ### so the intercepts among groups are different Coefficients: Estimate Std. Error t value Pr(>|t|) (Intercept) -7.21091 2.55094 -2.827 0.00858 ** Temp 3.60275 0.09729 37.032 < 2e-16 *** Speciesniv -10.06529 0.73526 -13.689 6.27e-14 *** ### but the calculated results will be identical. ### The slope estimate is the same. ### The intercept for species 1 (ex) is (intercept). ### The intercept for species 2 (niv) is (intercept) + Speciesniv. ### This is determined from the contrast coding of the Species ### variable shown below, and the fact that Speciesniv is shown in ### coefficient table above. niv ex 0 niv 1
ФтКЯЯпЕФМђЕЅЭМНт
plot(x = Data$Temp, y = Data$Pulse, col = Data$Species, pch = 16, xlab = "Temperature", ylab = "Pulse")
ФЃаЭЕФpжЕКЭRЦНЗН
Multiple R-squared: 0.9896, Adjusted R-squared: 0.9888 F-statistic: 1331 on 2 and 28 DF, p-value: < 2.2e-16
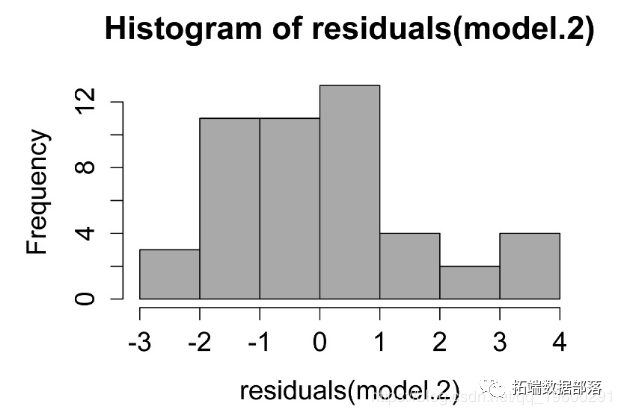
МьВщФЃаЭЕФМйЩш
ЯпадФЃаЭжаВаВюЕФжБЗНЭМЁЃетаЉВаВюЕФЗжВМгІНќЫЦе§ЬЌЁЃ
ВаВюгыдЄВтжЕЕФЙиЯЕЭМЁЃВаВюгІЮоЦЋЧвОљЕШЁЃ
### additional model checking plots with: plot(model.2) ### alternative: library(FSA); residPlot(model.2)
ОпгаШ§РрКЭIIаЭЦНЗНКЭЕФаЗНВюЪОР§ЗжЮі
БОЪОР§ЪЙгУIIаЭЦНЗНКЭЃЌВЂПМТЧОпгаШ§ИізщЕФЧщПіЁЃ
### -------------------------------------------------------------- ### Analysis of covariance, hypothetical data ### -------------------------------------------------------------- Data = read.table(textConnection(Input),header=TRUE) plot(x = Data$Temp, y = Data$Pulse, col = Data$Species, pch = 16, xlab = "Temperature", ylab = "Pulse") legend('bottomright', legend = levels(Data$Species), col = 1:3, cex = 1, pch = 16)
аЗНВюЗжЮі
options(contrasts = c("contr.treatment", "contr.poly")) ### These are the default contrasts in R Anova(model.1, type="II") Sum Sq Df F value Pr(>F) Temp 7026.0 1 2452.4187 <2e-16 *** Species 7835.7 2 1367.5377 <2e-16 *** Temp:Species 5.2 2 0.9126 0.4093 ### Interaction is not significant, so the slope among groups ### is not different. Anova(model.2, type="II") Sum Sq Df F value Pr(>F) Temp 7026.0 1 2462.2 < 2.2e-16 *** Species 7835.7 2 1373.0 < 2.2e-16 *** Residuals 125.6 44 ### The category variable (Species) is significant, ### so the intercepts among groups are different summary(model.2) Coefficients: Estimate Std. Error t value Pr(>|t|) (Intercept) -6.35729 1.90713 -3.333 0.00175 ** Temp 3.56961 0.07194 49.621 < 2e-16 *** Speciesfake 19.81429 0.66333 29.871 < 2e-16 *** Speciesniv -10.18571 0.66333 -15.355 < 2e-16 *** ### The slope estimate is the Temp coefficient. ### The intercept for species 1 (ex) is (intercept). ### The intercept for species 2 (fake) is (intercept) + Speciesfake. ### The intercept for species 3 (niv) is (intercept) + Speciesniv. ### This is determined from the contrast coding of the Species ### variable shown below. contrasts(Data$Species) fake niv ex 0 0 fake 1 0 niv 0 1
ФтКЯЯпЕФМђЕЅЭМНт
зщКЯФЃаЭЕФpжЕКЭRЦНЗН
Multiple R-squared: 0.9919, Adjusted R-squared: 0.9913 F-statistic: 1791 on 3 and 44 DF, p-value: < 2.2e-16
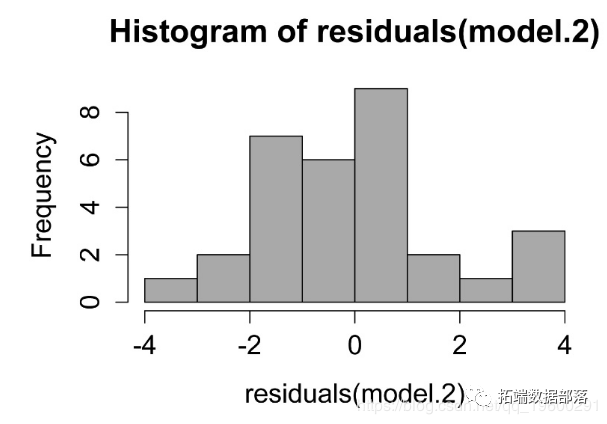
МьВщФЃаЭЕФМйЩш
hist(residuals(model.2), col="darkgray")
ЯпадФЃаЭжаВаВюЕФжБЗНЭМЁЃетаЉВаВюЕФЗжВМгІНќЫЦе§ЬЌЁЃ
plot(fitted(model.2), residuals(model.2))
ВаВюгыдЄВтжЕЕФЙиЯЕЭМЁЃВаВюгІЮоЦЋЧвОљЕШЁЃ
### additional model checking plots with: plot(model.2) ### alternative: library(FSA); residPlot(model.2)